Tim dr Zana Luthey‑Schultena razvio je 3D dinamičku simulaciju minimalne bakterije JCVI‑syn3A (493 gena) koja rekonstruiše ceo 105‑minutni ćelijski ciklus sa preciznošću od oko dve minute. Model kombinuje stohastičke reakcije, obične diferencijalne jednačine i Brownove dinamike da bi prikazao replikaciju DNK, sintezu proteina i promene oblika ćelije. Simulacija otkriva koordinaciju između transkripcije i metabolizma, ali ima ograničenja (ne prati atome i ne modeluje polisome). Renderovanje jednog ciklusa zahtevalo je veliki računski resurs: oko šest dana na dva GPU‑a i preko 15.000 GPU‑sati za 50 ćelija.
Najdetaljnija 3D Simulacija Života: Ceo Ćelijski Ciklus Minimalne Bakterije JCVI‑syn3A (493 Gena)

Tim istraživača predvođen dr Zan Luthey‑Schultenom razvio je trodimenzionalnu, potpuno dinamičnu računarsku simulaciju minimalne bakterije JCVI‑syn3A koja rekonstruiše čitav 105‑minutni ćelijski ciklus sa izuzetnom preciznošću.
Šta je Syn3A?
JCVI‑syn3A je minimalni sintetizovani organizam razvijen u J. Craig Venter Institute; njegov genom sadrži samo 493 gena organizovanih u jedan kružni molekul DNK, što ga čini pogodnim modelom za detaljnu simulaciju osnovnih životnih procesa.

Kako izgleda simulacija
Model kombinuje više računarskih pristupa: stohastičke metode za pojedine metaboličke reakcije, obične diferencijalne jednačine za druge procese i Brownove (Braunove) dinamike za pokrete DNK. Simulacija prikazuje ponašanje DNK kao fleksibilnog polimera koji se uvija, replikuje i deli u dve kopije, formiranje i kretanje ribosoma u citoplazmi, agregaciju membranskih proteina i promenu oblika ćelije od sferične do izdužene pre podele.
„Ovo je trodimenzionalan, potpuno dinamičan kinetički model minimalnog oblika života koji simulira ćelijsku aktivnost i razvoj,“ rekao je dr Luthey‑Schulten.
Validacija i rezultati
Virtualna ćelija ponašala se vrlo slično stvarnoj: predviđeni i eksperimentalni ciklusi razlikovali su se za oko dve minute. U simulaciji je replikacija DNK trajala oko 51 minut, a ćelija je udvostručila membransku površinu tokom 105‑minutnog ciklusa, što odgovara merenjima kod Syn3A. Eksperimentalna snimanja koja su sproveli Angad Mehta i Taekjip Ha potvrdila su simetričnu deobu ćelije i pomogla u konfiguraciji modela.
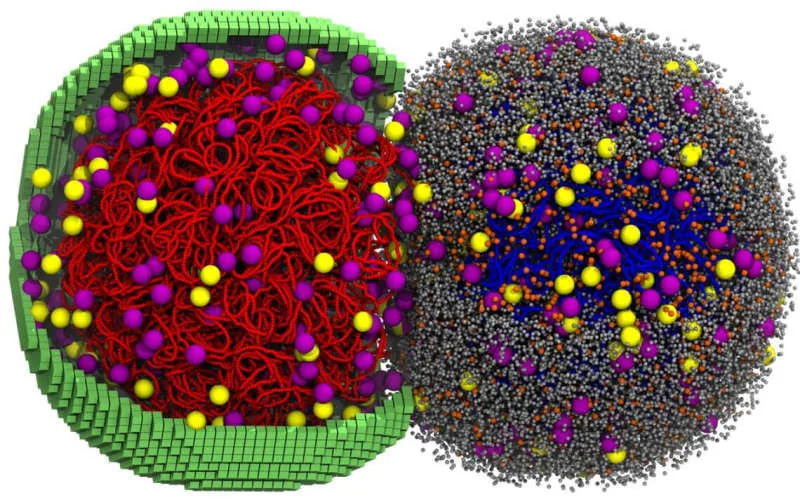
Tehnička i konceptualna otkrića
Model ističe da ćelije nisu homogeni kemijski reaktori: unutrašnjost je zbijena i heterogena, pa molekuli moraju difundovati i susretati se u prostoru da bi reakcije nastupile. Simulacija otkriva koordinaciju između transkripcije i metabolizma — oskudni nivoi nukleozid trifosfata dovode do "uključi‑isključi" obrazaca u transkripciji. U modelu je aktivnost ribosoma bila oko 55% vremena, dok je približno 70% RNK‑polimeraza bilo angažovano u transkripciji.
Ograničenja i resursi
Model ne prati pokrete pojedinačnih atoma: ponašanje je aproksimirano prosečnim vrednostima kako bi računanja bila održiva. Nisu modelovane sve pojave, na primer simultana translacija više mRNK u polisomima. Replikacija DNK bila je usko grlo performansi — istraživač Andrew Maytin prebacio je taj deo na namenski GPU kako bi ubrzao izvođenje; kompletan ciklus simulacije zahtevao je oko šest dana na dva visokoperformantna GPU‑a (u praksi 4–6 dana). Ukupno je za 50 simulisanih ćelija potrošeno preko 15.000 GPU‑sati.
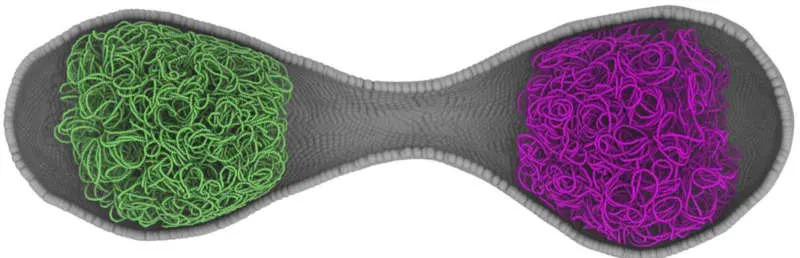
Zašto je ovo važno
Ova digitalna ćelija nudi četvorodimenzionalni uvid u međusobno delovanje molekularnih procesa u prostoru i vremenu i predstavlja okvir za buduće prediktivne virtualne ćelije. Takvi modeli mogu pomoći da se razume kako genetske promene utiču na ćelijske osobine, ubrzati dizajn sintetičkih organizama i osvetliti osnovne principe života.
Rezultati su objavljeni u časopisu Cell (članak oznake Cell00174‑1).
Pomozite nam da budemo bolji.